视觉基因组 (Visual Genome)
视觉基因组使用说明
视觉基因组可以理解为“先依次选好区域、属性、关系,再框选图像”:按顺序在「区域」「属性」「关系」三栏中分别点选对应标签后,再在图像上用矩形框标出目标区域;框选完成后,系统会结合所选标签自动生成与该区域相关的描述信息。它适合复杂场景理解任务,比如图像描述生成、视觉问答、关系推理与多模态训练等场景。
标注核心作用
- 同时建模对象与语义关系:不仅知道“有什么”,还知道“是什么样”和“彼此关系”;
- 支持分栏标签管理:区域、属性、关系分组展示,降低复杂标注任务的操作负担;
- 提升数据表达能力:相比单一检测标注,更适合高阶语义理解任务。
基础操作步骤
- 在「区域」栏选择目标描述标签;
- 在「属性」栏选择属性标签;
- 在「关系」栏选择关系标签;
- 在图像上框选对应区域;框选完成后,系统会自动生成与该区域相关的描述信息。
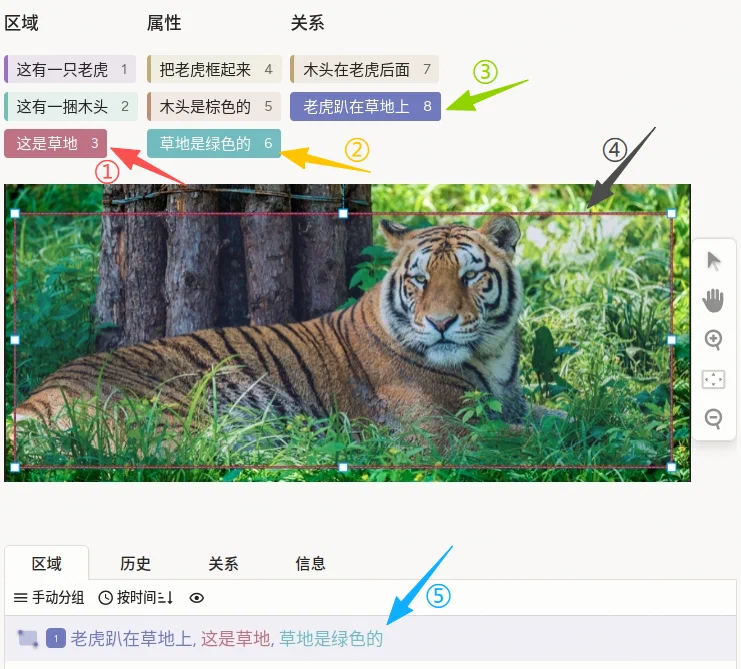
说明:请按「区域 → 属性 → 关系」的顺序依次选择标签后再框选,便于生成描述与标签一致;若需标注多个目标,可重复上述流程。
注意事项
- 区域标签应准确对应可见目标,避免一个标签覆盖多个不相关对象;
- 属性标签需与对象本身一致,避免将关系信息写入属性;
- 关系标签建议使用统一表达口径,减少同义描述带来的数据噪声。
模板预览

模板配置
完整代码块
<View>
<View style="display: flex; flex-wrap: wrap;">
<View className="label-column">
<Header value="区域"/>
<RectangleLabels name="regions" toName="image" value="$regions"/>
</View>
<View className="label-column">
<Header value="属性"/>
<RectangleLabels name="attributes" toName="image" value="$attributes"/>
</View>
<View className="label-column">
<Header value="关系"/>
<RectangleLabels name="relationships" toName="image" value="$relationships"/>
</View>
</View>
<Image name="image" value="$image_path"/>
<Style>
.label-column .lsf-labels {
display: flex;
flex-direction: column;
align-items: flex-start;
}
</Style>
</View>视觉基因组配置代码说明
以上代码用于实现“区域/属性/关系”三类标签的分栏展示与标注,适合语义层次较丰富的图像任务。
1、分栏标签区:通过多个 RectangleLabels 组件分别承载区域、属性、关系标签,并使用 value="$regions"、value="$attributes"、value="$relationships" 动态注入标签集合。
2、图片组件:Image 用于加载待标注图像。
3、样式组件:Style 将每个分栏内标签改为纵向排列,提升可读性和选择效率。
示例数据(简要)
以下示例数据用于说明如何向模板传入图像地址和三类标签列表,可按项目需要替换具体内容。
{
"data": {
"image_path": "/static/templates/project-templates-config/computer-vision/visual-genome/visual-genome.png",
"regions": [
{ "value": "这有一只老虎" },
{ "value": "这有一捆木头" },
{ "value": "这是草地" }
],
"attributes": [
{ "value": "把老虎框起来" },
{ "value": "木头是棕色的" },
{ "value": "草地是绿色的" }
],
"relationships": [
{ "value": "木头在老虎后面" },
{ "value": "老虎趴在草地上" }
]
}
}说明
- 代码可直接复制到标注配置文件中使用;
- 三类标签可按业务增删,保持字段名与模板配置一致即可;
- 建议先统一标签命名规范,再批量开展标注。